微生物測序
微生物組(Microbiome)是指一個特定環(huán)境或生態(tài)系統(tǒng)中全部微生物及其遺傳信息的集合,?蘊藏著極為豐富的微生物資源。全面系統(tǒng)地解析微生物組的結(jié)構(gòu)和功能,?將為解決人類面臨的能源、生態(tài)環(huán)境、工農(nóng)業(yè)生產(chǎn)和人體健康等重大問題帶來新思路
細菌完成圖(三代測序)
基因組是闡釋生命現(xiàn)象和揭示生命規(guī)律的重要手段,三代PacBio HiFi測序模式可產(chǎn)生既兼顧長讀長,又具有高精度的測序結(jié)果,貝瑞基因HiFi細菌完成圖測序,即利用PacBio HiFi測序模式對細菌物種進行基因組de novo組裝,從而獲得該細菌種完整基因組序列,該技術(shù)大大提升了細菌基因組組裝的完整性和準確性,可真正實現(xiàn)細菌0 gap組裝。
真菌精細圖(三代測序)
三代真菌精細圖,即采用PacBio測序平臺,利用高深度三代數(shù)據(jù)進行真菌基因組de novo組裝,獲得真菌基因組序列信息的一種技術(shù)手段。真菌基因組一般在10M-150M,有多核和雜合等現(xiàn)象,利用三代測序技術(shù)的優(yōu)勢破譯真菌基因組,能克服二代測序?qū)Ω逩C、高重復、高雜合位置檢出不準確的現(xiàn)象,得到更加完整和均勻的基因組,結(jié)合HiC輔助組裝技術(shù)可獲得染色體水平全基因組序列圖譜,此外,測序同時還可獲得甲基化修飾位點信息。
全長16s(三代測序)
常規(guī)二代16S僅針對單個可變區(qū)或者連續(xù)兩到三個可變區(qū)進行測序,而基于PacBio HiFi測序的全長16S(V1-V9)可獲取微生物16S的全長序列,突破了二代測序讀長較短的局限性,能夠更好的實現(xiàn)微生物在種水平上的分類, 可獲得物種分類、豐度、種群結(jié)構(gòu)等更加深入和全面的信息。基于PacBio HiFi測序技術(shù)的全長16s測序為微生物多樣性研究提供了強有力的技術(shù)手段。
宏基因組(二代測序)
二代宏基因組測序技術(shù)是依托二代測序平臺以特定環(huán)境中的整個微生物群落作為研究的對象,不需要對微生物進行分離培養(yǎng),提取環(huán)境微生物總DNA進行研究,進行微生物群體的物種分類、復雜度分析、群落結(jié)構(gòu)、功能注釋、樣品間的物種或基因差異及物種間的代謝網(wǎng)絡(luò)研究。與傳統(tǒng)微生物研究方法相比,宏基因組測序技術(shù)規(guī)避了絕大部分微生物不能培養(yǎng)、痕量菌無法檢測的缺點。
應用方向
- 精準醫(yī)療:探究腸道、皮膚、陰道等菌群環(huán)境對疾病的影響,尋找與代謝類疾病、消化類疾病、自身免疫性疾病等相關(guān)的biomarker及與癌癥相關(guān)的治療靶點;
- 藥物代謝:探究功能食品、中藥的體內(nèi)代謝及藥效機制;
- 傳統(tǒng)發(fā)酵生產(chǎn):關(guān)鍵風味物質(zhì)溯源及控制發(fā)酵微生物菌種優(yōu)化改良,及特殊功能菌株、基因挖掘、工程菌開發(fā)等;
- 畜牧漁養(yǎng)殖:研究腸道、瘤胃等微生物與動物繁殖、生長發(fā)育、營養(yǎng)健康、免疫和疾病治療等的互作關(guān)系、對環(huán)境的響應及對生產(chǎn)的影響;
- 大農(nóng)業(yè):研究根系微生物對植物生長、抗逆的影響,指導種植方式;
- 環(huán)境領(lǐng)域:研究特定環(huán)境下微生物研究,解決有機肥發(fā)酵處理、污水治理、石油降解、水體及海洋環(huán)境等環(huán)境相關(guān)問題;
案例解析
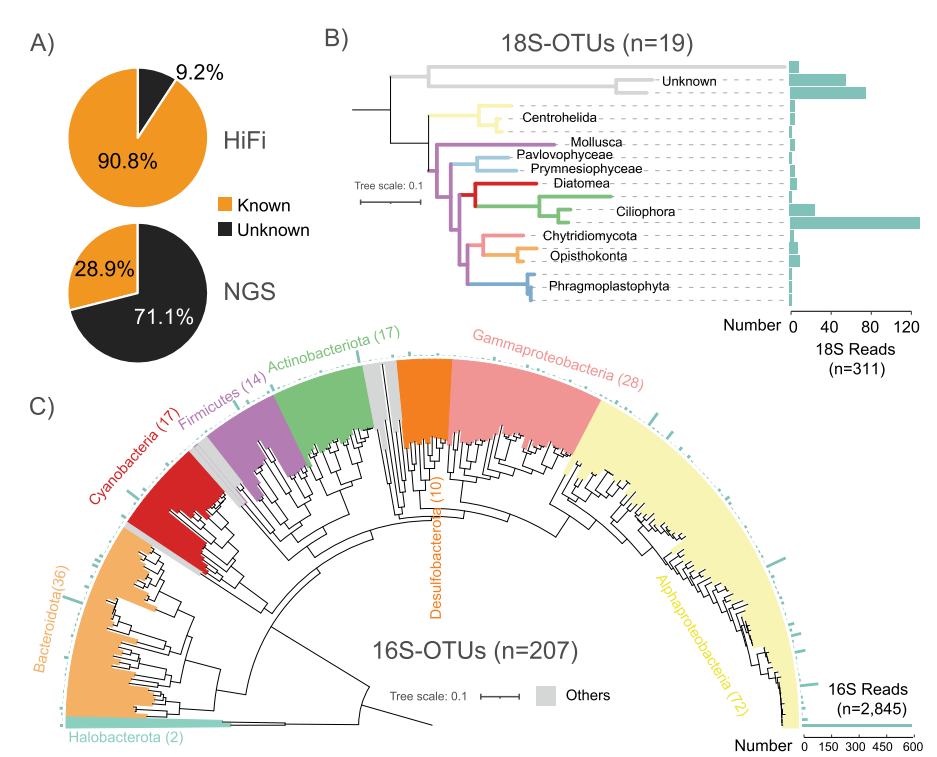
基于HiFi reads的分類分辨率。(A) HiFi和NGS讀數(shù)具有(已知)/不具有(未知)分類信息的百分比。(B和C)基于19個全長18S-OTUs (B)和207個全長16S-OTUs (C)的系統(tǒng)進化樹
利用HiFi宏基因組測序技術(shù)改進西藏鹽湖沉積物中宏基因組組裝和病毒組裝
該文通過應用長讀長測序技術(shù)和短讀長測序技術(shù)對青藏高原鹽湖沉積物樣品進行測序,評估了不同組裝策略在宏基因組組裝和病毒組裝中的性能。28.9% 的 NGS 讀取可以分配到已知的分類等級,而HiFi數(shù)據(jù)的讀取分配率為90.8%,大約是NGS的三倍。HiFi reads的物種級別分配率為67.19%,而短讀長的相應比率僅為5.59%,說明HiFi reads在分類方面的強大能力。總共鑒定出17個最小相對豐度大于0.1%的門,大大超過了NGS技術(shù)的檢索性能。這為復雜環(huán)境樣品的物種組成研究,特別是對真核微生物的了解提供了便利。
參考文獻:Tao Y, Xun F, Zhao C, Mao Z, et al. Improved Assembly of Metagenome-Assembled Genomes and Viruses in Tibetan Saline Lake Sediment by HiFi Metagenomic Sequencing. Microbiol Spectr. 2023 Feb 14;11(1):e0332822.

